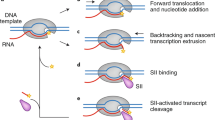
Abstract
In eukaryotes three major nuclear RNA Polymerases (Pols I, II and III) transcribe the genome. Pols II and III transcribe many different genes. Pol I has only one target from which it synthesizes the precursor for 3 of 4 ribosomal (r)RNAs accounting for up to 60 percent of total cellular RNA. Dedication of Pol I and its specific transcription factors to transcribe a single gene underlines the importance of rRNA synthesis. Research in Regensburg aims at understanding mechanism(s) of Pol I transcription.
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Warner JR (1999) The economics of ribosome biosynthesis in yeast. Trends Biochem Sci 24: 437–440
Nomura M, Nogi Y, Oakes M (2013) Transcription of rDNA in the yeast Saccharomyces cerevisiae. In: Madame Curie Bioscience Database. Landes Bioscience, Austin (TX); 2000–2013
Cormack BP, Struhl K (1992) The TATA-binding protein is required for transcription by all three nuclear RNA polymerases in yeast cells. Cell 69: 685–696
Reiter A, Hamperl S, Seitz H et al. (2012) The Reb1-homologue Ydr026c/Nsi1 is required for efficient RNA polymerase I termination in yeast. EMBO J 31: 3480–3493
Engel C, Sainsbury S, Cheung AC et al. (2013) RNA polymerase I structure and transcription regulation. Nature 502: 650–655
Girbig M, Misiaszek AD, Müller CW (2022) Structural insights into nuclear transcription by eukaryotic DNA-dependent RNA polymerases. Nat Rev Mol Cell Biol, DOI: https://doi.org/10.1038/s41580-022-00476-9
Engel C, Plitzko J, Cramer P (2016) RNA polymerase I-Rrn3 complex at 4.8 A resolution. Nat Commun 7: 12129
Pilsl M, Crucifix C, Papai G et al. (2016) Structure of the initiation-competent RNA polymerase I and its implication for transcription. Nat Commun 7: 12126
Pilsl M, Engel C (2020) Structural basis of RNA polymerase I pre-initiation complex formation and promoter melting. Nat Commun 11: 1206
Engel C, Gubbey T, Neyer S et al. (2017) Structural basis of RNA polymerase I transcription initiation. Cell 169: 120–131.e22
Heiss FB, Daiß JL, Becker P et al. (2021) Conserved strategies of RNA polymerase I hibernation and activation. Nat Commun 12: 758
Baudin F, Murciano B, Fung HKH et al. (2022) Mechanism of RNA polymerase I selection by transcription factor UAF. Sci Adv 8: eabn5725
Hamperl S, Wittner M, Babl V et al. (2013) Chromatin states at ribosomal DNA loci. Biochim Biophys Acta 1829: 405–417
Merkl PE, Pilsl M, Fremter T et al. (2020) RNA polymerase I (Pol I) passage through nucleosomes depends on Pol I subunits binding its lobe structure. J Biol Chem 295: 4782–4795
Hamperl S, Brown CR, Garea AV et al. (2014) Compositional and structural analysis of selected chromosomal domains from Saccharomyces cerevisiae. Nucleic Acids Res 42: e2
Götze H (2010) Function of the upstream activating factor in chromatin structure organization and transcriptional regulation at the yeast ribosomal DNA. PhD thesis, University of Regensburg
Reiter A, Steinbauer R, Philippi A et al. (2011) Reduction in ribosomal protein synthesis is sufficient to explain major effects on ribosome production after short-term TOR inactivation in Saccharomyces cerevisiae. Mol Cell Biol 31:803–817
Funding
Open Access funding enabled and organized by Projekt DEAL.
Author information
Authors and Affiliations
Corresponding author
Additional information
Michael Pilsl (M.P.) Jahrgang 1986. Biologiestudium In Regensburg. 2021 Promotion In Biochemie, Universität Regensburg. Seit 2021 Postdoc am Regensburg Center for Biochemistry (RCB), Universität Regensburg.
Herbert Tschochner (H.T.) Jahrgang 1957. Biologiestudium in Regensburg. 1987 Promotion in Biochemie, Universität Regensburg. 1988–1989 Postdoc Lehrstuhl Biochemie I, Universität Regensburg. 1989–1992 Postdoc am Department of Structural Biology, Stanford University, USA. 1992–2003 Forschungsgruppenleiter Biochemiezentrum Universität Heidelberg. Seit 2003 Leiter des Lehrstuhls Biochemie III am Regensburg Center for Biochemistry (RCB), Universität Regensburg.
Joachim Griesenbeck (J.G.) Jahrgang 1967. Chemiestudium in Freiburg. 1998 Promotion in Biochemie, FU Berlin. 1998–2004 Postdoc am Department of Structural Biology, Stanford University, USA. 2004–2016 Arbeitsgruppenleiter am Lehrstuhl Biochemie III der Universität Regensburg. Seit 2016 Außerplanmäßiger Professor am Lehrstuhl Biochemie III am Regensburg Center for Biochemistry (RCB), Universität Regensburg.
Christoph Engel (C.E.) Jahrgang 1985. Studium Molekulare Biotechnologie in Heidelberg. 2014 Promotion in Strukturbiologie am Genzentrum der LMU München. 2014–2017 PostDoc am Max-Planck-Institut für Biophysikalische Chemie in Göttingen. Seit 2018 Emmy-Noether Forschungsgruppenleiter an der Universität Regensburg und seit 2019 Tenure Track Professor für Strukturelle Biochemie.
Rights and permissions
Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
Pilsl, M., Tschochner, H., Griesenbeck, J. et al. RNA-Polymerase I: einer spezialisierten Transkriptionsmaschine auf der Spur. Biospektrum 28, 484–487 (2022). https://doi.org/10.1007/s12268-022-1809-3
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-022-1809-3